L’équipe biobanque est composée de
> 4 techniciens
> 2 ingénieurs
> 1 cadre
> 1 responsable biologiste
À consulter : Charte plateforme Génomique
L’activité de séquençage des acides nucléiques d’agents infectieux a été initiée dès 1993 dans les laboratoires de diagnostic et de recherche actuellement regroupés au sein de l’IHU Méditerranée Infection. Les technologies de séquençage de nouvelle génération y ont été introduites dès 2006.
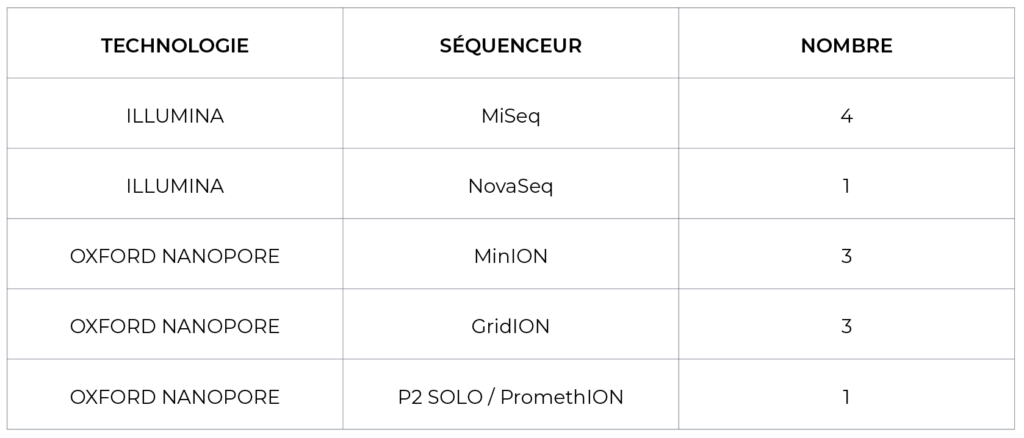
La plateforme actuelle de séquençage de nouvelle génération et génomique utilise les technologies Illumina et Oxford Nanopore. Elle est le support d’un nombre important de projets de recherches comprenant le séquençage de génomes complets ou partiels de virus, bactéries, champignons et parasites, et de métagénomes (séquençage de tous les acides nucléiques) à partir d’échantillons cliniques ou de cultures virales ou microbiennes. Ces projets permettent d’identifier des agents infectieux connus, génétiquement divergents, et nouveaux ; de caractériser leurs génomes et leur évolution ; de caractériser les éléments associés à la transmissibilité, à la pathogénicité, et à la sensibilité aux traitements.
L’IHU Méditerranée Infection reçoit tous les prélèvements à caractère infectieux de l’Assistance Publique des Hôpitaux de Marseille (APHM) comprenant le Centre Hospitalier de la Timone, l’Hôpital Nord, l’Hôpital de la Conception, les Hôpitaux Sud (Sainte-Marguerite et Salvator) ainsi que l’Espace Santé (lieu de santé hors les murs, dans des lieux de vie les plus défavorisés). Il reçoit également des prélèvements extérieurs provenant de laboratoires de ville pour mener des recherches plus approfondies que ce qui peut être fait dans leurs locaux. La fondation est divisée en 4 pôles majeurs de recherche : la bactériologie, la virologie, la parasitologie-mycologie et l’immuno-allergologie. Les prélèvements reçus peuvent être liquides ou solides et sont de natures très diverses : sérum, selles, liquide céphalo-rachidien (LCR), valves, oeil, crachat, plasma, os, etc. L’ensemble de ces tubes est aliquoté à la réception de l’Institut dans des tubes codés ayant une contenance de 0.7mL à 2mL. Ces tubes sont spécifiques aux automates de la biobanques pour être stockés de façon optimale.

La société Enovacom, filiale d’Orange spécialisée dans la création de logiciels informatiques, a mis au point un logiciel sur mesure : Biobank Middleware, capable de faire le lien entre le code 1D crée par le logiciel intra-hospitalier et le code 2D unique gravé sur les tubes. Celui-ci est capable d’intégrer les automates au circuit de soin de l’IHU. Le code 2D étant la seule information lue par la biobanque automatisée, ce lien est indispensable pour ne pas perdre les données associées. Les données sont pseudonymisées afin de pouvoir remonter jusqu’au patient grâce à ce code 2D. Les données saisies sont ensuite envoyées au logiciel associé aux automates.

Amrane S, Hocquart M, Afouda P, Kuete E, Pham TP, Dione N, Ngom II, Valles C, Bachar D, Raoult D, Lagier JC. Metagenomic and culturomic analysis of gut microbiota dysbiosis during Clostridium difficile infection. Sci Rep. 2019 Sep 5;9(1):12807. doi: 10.1038/s41598-019-49189-8. PMID: 31488869.
Baron SA, Cassir N, Hamel M, Hadjadj L, Saidani N, Dubourg G, Rolain JM. Risk factors for acquisition of colistin-resistant Klebsiella pneumoniae and expansion of a colistin-resistant ST307 epidemic clone in hospitals in Marseille, France, 2014 to 2017.Euro Surveill. 2021 May;26(21):2000022. doi: 10.2807/1560-7917.ES.2021.26.21.2000022. PMID: 34047270.
Colson P, Penant G, Delerce J, Boschi C, Wurtz N, Bedotto M, Branger S, Brouqui P, Parola P, Lagier JC, Cassir N, Tissot-Dupont H, Million M, Aherfi S, La Scola B. Sequencing of monkeypox virus from infected patients reveals viral genomes with APOBEC3-like editing, gene inactivation, and bacterial agents of skin superinfection. J Med Virol. 2023 Jun;95(6):e28799. doi: 10.1002/jmv.28799. PMID: 37342884.
Colson P, Fournier PE, Chaudet H, Delerce J, Giraud-Gatineau A, Houhamdi L, Andrieu C, Brechard L, Bedotto M, Prudent E, Gazin C, Beye M, Burel E, Dudouet P, Tissot-Dupont H, Gautret P, Lagier JC, Million M, Brouqui P, Parola P, Fenollar F, Drancourt M, La Scola B, Levasseur A, Raoult D. Analysis of SARS-CoV-2 Variants From 24,181 Patients Exemplifies the Role of Globalization and Zoonosis in Pandemics. Front Microbiol. 2022 Feb 7;12:786233. doi: 10.3389/fmicb.2021.786233. PMID: 35197938.
Morsli M, Boudet A, Kerharo Q, Stephan R, Salipante F, Dunyach-Remy C, Houhamdi L, Fournier PE, Lavigne JP, Drancourt M. Real-time metagenomics-based diagnosis of community-acquired meningitis: A prospective series, southern France. EBioMedicine. 2022 Oct;84:104247. doi: 10.1016/j.ebiom.2022.104247. PMID: 36087524.